Visão Geral Mais Abrangente do scTCR Seq: Compreendendo a Sequenciação de Receptores de Células T de Célula Única
Célula única Sequenciação do recetor de células T (scTCR Seq) representa um avanço pioneiro no estudo das respostas imunes. Esta tecnologia permite a análise dos TCRs a nível de célula única, proporcionando uma visão detalhada da diversidade e especificidade das células T. Tais insights detalhados são críticos para o avanço da pesquisa em oncologia, distúrbios autoimunes e no desenvolvimento de imunoterapias personalizadas. Este artigo explora a importância, aplicações e benefícios do scTCR Seq, elucidando o seu impacto transformador no campo da imunologia.
O que é scTCR Seq?
scTCR Seq é um avanço metodológico sofisticado que permite aos investigadores analisar o repertório do receptor de células T (TCR) com uma resolução de célula única sem precedentes. Esta abordagem captura eficazmente a intrincada diversidade e especificidade das respostas das células T em uma variedade de contextos biológicos, incluindo malignidades, agentes infecciosos e distúrbios autoimunes. Através da isolação e sequenciação de células T individuais, o scTCR Seq facilita uma compreensão profunda das operações do sistema imunológico a nível celular.
Por que é importante?
Sequenciação convencional de TCR As metodologias geralmente avaliam TCRs derivados de populações de células T em massa, proporcionando uma visão geral generalizada da diversidade dos recetores. Em contraste, o scTCR Seq fornece dados precisos e abrangentes sobre os perfis de recetores de células T individuais, abrangendo tanto as cadeias alfa como beta do TCR. Este nível de detalhe oferece insights significativos sobre a clonalidade das células T e as respostas funcionais, que são vitais para a progressão de abordagens médicas personalizadas e o aprimoramento das imunoterapias contra o câncer.
Para mais informações sobre a sequenciação de TCR e as suas contribuições para a investigação imunológica, os leitores interessados são incentivados a explorar a nossa página dedicada em Serviços de Sequenciação de TCR.
Vantagens do scTCR Seq em Relação ao Sequenciamento Tradicional de TCR
Sequenciação de Cadeias TCR Emparelhadas
A sequenciação scTCR-seq oferece a identificação precisa de clonótipos de células T, permitindo que os investigadores determinem com precisão os emparelhamentos das cadeias α e β dentro de células T individuais. Esta capacidade é crucial para compreender a especificidade e a função das células T. Stubbington et al. exemplificaram a eficácia da sequenciação emparelhada de TCR na identificação de células T específicas para antígenos no contexto de um estudo sobre infecção por Salmonella.
Integração com Transcriptómica
A integração do scTCR-seq com perfilamento transcriptómico facilita a ligação das sequências de TCR aos padrões de expressão génica, proporcionando insights valiosos sobre a funcionalidade das células T. Esta correlação oferece uma perspetiva holística sobre a biologia das células T. Zhang et al. empregaram com sucesso esta metodologia para delinear assinaturas transcricionais distintas relacionadas com diferentes clonótipos de TCR em linfócitos infiltrantes tumorais.
Capacidade de Alto Rendimento
A natureza de alto rendimento das modernas plataformas de scTCR-seq permite a análise simultânea de milhares de células dentro de um único ambiente experimental. Esta capacidade é fundamental para o perfilamento abrangente das populações de células T. O trabalho de Zheng et al., utilizando uma abordagem baseada em gotículas, destacou a capacidade de processar mais de 5.000 células T individuais em um único experimento.
Alta Resolução
O ScTCR-seq oferece uma resolução excecional na investigação da heterogeneidade das células T, fornecendo informações sobre a diversidade e a expansão clonal das células T a nível de célula única. Esta análise de alta resolução foi demonstrada num estudo de Guo et al., que revelou a arquitetura clonal das células T infiltrantes tumorais no câncer colorretal.
Análise Clonal
O emparelhamento preciso das cadeias TCR α e β possibilitado pelo scTCR-seq é fundamental para compreender as respostas imunes. Wu et al. aproveitaram esta capacidade para examinar 47 biópsias tumorais de pacientes com cancro do pulmão de não pequenas células, revelando insights críticos sobre a dinâmica das células T durante a imunoterapia.
Ligação de Funcionalidades
Esta técnica permite a associação das funções das células T—como a citotoxicidade e a produção de citocinas—com TCRs específicos. Em pacientes com melanoma submetidos a terapia de bloqueio de pontos de verificação, Yost et al. utilizaram scTCR-seq para rastrear clones de células T, ilustrando assim a relação entre a expansão clonal e os fenótipos funcionais.
Design de Imunoterapia Aprimorada
O scTCR-seq oferece insights fundamentais críticos para o design de imunoterapias direcionadas. A aplicação do scTCR-seq por Penter et al. para analisar produtos de células CAR-T revelou informações vitais sobre a sua composição clonal e potencial eficácia, fornecendo orientação para o desenvolvimento de terapias celulares mais eficazes. Esta ferramenta de ponta está a revolucionar a investigação em domínios como a imunoterapia, o desenvolvimento de vacinas e a medicina de transplantes. Notavelmente, o uso do scTCR-seq por Yost et al. para monitorizar a dinâmica de clones individuais de células T durante a terapia de bloqueio de pontos de controlo na imunoterapia do câncer elucidou os mecanismos subjacentes às respostas ao tratamento e à resistência.
Com estas capacidades inovadoras, o scTCR-seq está a abrir caminho para novas descobertas em investigação imunológica e desenvolvimento de terapias.
Como funciona o scTCR Seq
O processo de sequenciação de scTCR, embora complexo, oferece profundas percepções sobre as respostas imunes ao elucidar os perfis detalhados dos recetores de células T. Abaixo está uma visão sistemática dos passos chave envolvidos:
Isolamento de Células
A iniciação do sequenciamento de scTCR envolve a isolação de células T individuais, um passo crítico alcançado através de técnicas avançadas como microfluídica ou separação celular por fluorescência (FACS). Este passo garante o processamento compartimentalizado de cada célula T, mantendo a integridade e a especificidade das análises subsequentes.
Amplificação de TCR
Após a isolação, os genes TCR, abrangendo tanto as cadeias alfa como beta, são amplificados através da Reação em Cadeia da Polimerase (PCR). Esta amplificação é crucial para gerar uma quantidade suficiente de material genético propício para sequenciação, facilitando o estudo detalhado dos TCRs.
Sequenciação
O sequências de TCR amplificadas são submetidos a tecnologias de Sequenciação de Nova Geração (NGS). Através deste passo, os investigadores podem identificar e caracterizar com precisão os distintos TCRs presentes em células T individuais, permitindo uma compreensão abrangente da diversidade e especificidade dos recetores de células T.
Análise de Dados
Na fase final, são utilizadas ferramentas de bioinformática sofisticadas para processar e analisar o vasto corpus de dados de sequenciação gerados. Esta análise computacional ajuda na combinação das cadeias TCR alfa e beta e na identificação de clones de células T, fornecendo informações inestimáveis sobre o repertório imunitário.
O fluxo de trabalho de sequenciação de scTCR é altamente detalhado e necessita da utilização de tecnologias de ponta.
Para uma análise aprofundada das estratégias de perfilagem de TCR, consulte o nosso artigo sobre Métodos de Detecção de TCREsta exploração destaca a versatilidade e precisão do sequenciamento de scTCR na promoção da nossa compreensão das respostas imunes.
 Figura 1 Visão geral esquemática do pipeline scTCRseq. (David Redmond) et al.,.2016)
Figura 1 Visão geral esquemática do pipeline scTCRseq. (David Redmond) et al.,.2016)
Análise de Dados de Sequenciação de scTCR
A análise dos dados de sequenciação de scTCR abrange várias etapas fundamentais, cada uma das quais é sustentada por evidências empíricas de investigações científicas recentes:
Controlo de Qualidade
Garantir leituras de sequenciamento de alta qualidade e a integridade celular é fundamental para alcançar análises fiáveis a montante. Por exemplo, Wu et al. enfatizaram este passo crítico na sua análise da dinâmica das células T durante a imunoterapia. Medidas rigorosas de controlo de qualidade foram implementadas para assegurar dados de sequenciamento de TCR fiáveis, sublinhando a necessidade de processos de filtragem rigorosos.
Montagem do TCR
A reconstrução de sequências completas de TCR constitui um componente vital da análise de scTCR-seq. Zheng et al. empregaram eficazmente este método ao perfilar 5.000 células T infiltradas por tumor de um paciente com câncer colorretal, integrando com sucesso sequências completas de TCR com dados de expressão génica. Este passo facilita uma compreensão mais detalhada das configurações do recetor de células T dentro do microambiente imunitário.
Identificação de Clonótipos
A identificação de clonótipos, ou grupos de células que partilham sequências idênticas de TCR, é essencial para decifrar a dinâmica das populações de células T. No seu estudo envolvendo pacientes com melanoma submetidos a terapia de bloqueio de pontos de controlo, Yost et al. utilizaram esta abordagem para elucidar padrões de expansão clonal, oferecendo novas perspetivas sobre os fundamentos mecânicos das respostas terapêuticas.
Análise da Diversidade
A análise da diversidade, que envolve a quantificação da clonalidade e da riqueza dentro das populações de células T, fornece informações críticas sobre a amplitude do repertório imunitário. Giang et al. aplicaram esta estratégia analítica na sua pesquisa sobre artrite reumatoide, revelando características únicas do TCR dentro de clones expandidos localizados em articulações inflamadas.
Integração do Transcriptoma
A integração de sequências de TCR com perfis de expressão génica oferece uma perspetiva abrangente sobre a biologia das células T. Waickman et al. ilustraram esta abordagem no seu estudo sobre células T específicas do vírus da dengue, onde associaram variações no repertório de TCR a perfis transcricionais ao longo do curso da infeção e da vacinação.
Ferramentas Populares para Análise de Dados scTCR-seq
Seurat: Uma ferramenta versátil amplamente utilizada para análise de células únicas, incluindo a integração de dados de TCR.
scRepertoire: Adaptado para a análise de repertórios de TCR em conjuntos de dados de células únicas.
TraCeR: Projetado para a reconstrução de sequências de recetores de células T a partir de dados de RNA-seq de célula única.
VDJtools: Fornece um conjunto abrangente de ferramentas para a pós-análise do sequenciamento do repertório imune.
Esta robusta suíte de estratégias e ferramentas analíticas sublinha o potencial transformador do scTCR-seq na promoção da nossa compreensão da biologia das células T e das respostas imunes.
Aplicações do scTCR Seq
Agora que vimos como funciona o scTCR-seq, vamos explorar como esta tecnologia é aplicada em várias áreas, desde a imunoterapia do cancro até às doenças autoimunes.
O scTCR-seq surgiu como uma ferramenta poderosa na investigação em imunologia, oferecendo insights sem precedentes sobre as respostas das células T em várias doenças e aplicações terapêuticas. Aqui estão algumas aplicações-chave do scTCR-seq suportadas por evidências científicas:
Imunoterapia do Câncer
O scTCR-seq revolucionou a nossa compreensão dos linfócitos infiltrantes tumorais (TILs) e do seu papel na imunoterapia do câncer. Wu et al. utilizaram scRNA-seq e scTCR-seq integrados para analisar 47 biópsias tumorais de 36 pacientes com câncer de pulmão não pequenas células antes e depois da terapia anti-PD-1.
Descobriram que os tumores responsivos apresentavam uma infiltração de células T CD8+ superior em comparação com os tumores não responsivos, e identificaram subpopulações distintas de células T associadas à resposta ao tratamento.
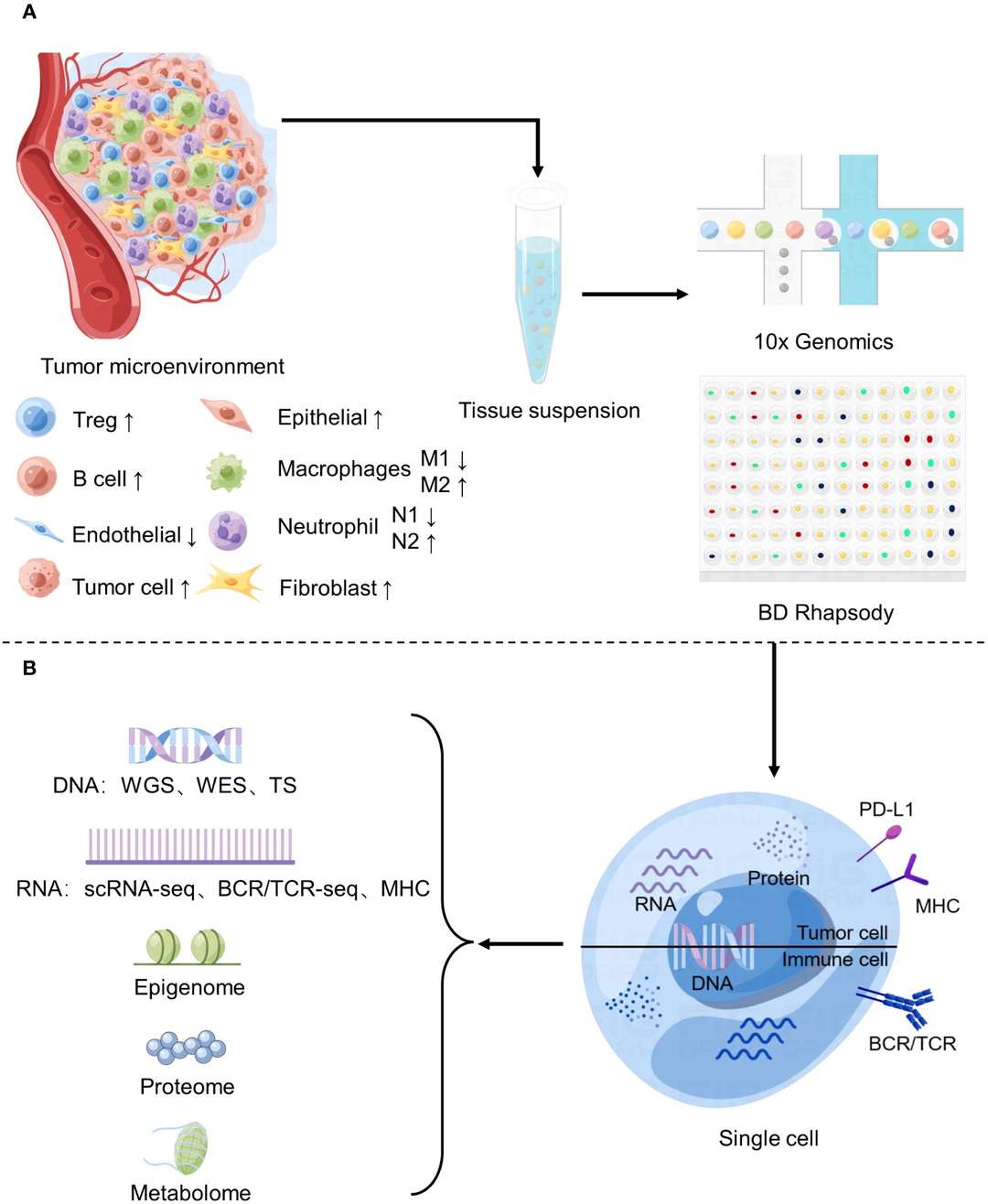 Figura 2 Aplicação do sequenciamento de célula única no estudo do microambiente tumoral.Sijie Chen et al.,. 2023)
Figura 2 Aplicação do sequenciamento de célula única no estudo do microambiente tumoral.Sijie Chen et al.,. 2023)
Doenças Autoimunes
Na investigação autoimune, o scTCR-seq ajuda a identificar clones de células T associados a doenças. Por exemplo, Giang et al. aplicaram o scTCR-seq para estudar células T na artrite reumatoide, revelando clones expandidos com características de TCR distintas em articulações inflamadas.
Doenças Infecciosas
O scTCR-seq tem sido fundamental no estudo das respostas das células T a infeções. Waickman et al. utilizaram o scTCR-seq para analisar células T específicas do vírus da dengue, fornecendo informações sobre as alterações no repertório de TCR durante a infeção e a vacinação.
Medicina Personalizada
A capacidade de perfilar os repertórios de TCR individuais dos pacientes torna o scTCR-seq valioso para a medicina personalizada. Yost et al. utilizaram o scTCR-seq para rastrear clones de células T em pacientes com melanoma submetidos a terapia de bloqueio de pontos de verificação, demonstrando seu potencial para prever respostas ao tratamento.
Monitorização de Doenças e Descoberta de Biomarcadores
A scTCR-seq pode identificar assinaturas imunes associadas à progressão da doença e descobrir assinaturas de TCR específicas da doença. Zhang et al. aplicaram a scTCR-seq para monitorizar a doença residual mínima em pacientes com leucemia mieloide aguda, demonstrando o seu potencial como um biomarcador sensível.
Desenvolvimento de Imunoterapia
Caracterizar TILs e células T engenheiradas é crucial para otimizar as imunoterapias contra o câncer. Penter et al. utilizaram scTCR-seq para estudar produtos de células CAR-T, revelando informações sobre a sua composição clonal e potencial eficácia.
Pesquisa de Vacinas
O scTCR-seq pode avaliar a eficácia da vacina ao analisar as respostas das células T. Minervina et al. aplicaram o scTCR-seq para estudar as respostas das células T à vacinação contra a gripe, fornecendo informações sobre a formação da memória imunológica.
Medicina de Transplante
Na transplantação, o scTCR-seq pode monitorizar a doença enxerto-versus-hospedeiro e a rejeição de órgãos. DeWolf et al. utilizaram o scTCR-seq para rastrear células T alorreativas em recetores de transplante de células estaminais, demonstrando o seu potencial para prever e gerir complicações. Estas aplicações destacam a versatilidade e o poder do scTCR-seq na promoção da nossa compreensão da biologia das células T e das suas implicações clínicas em várias áreas da medicina.
Para mais informações sobre o papel do scTCR Seq na medicina personalizada, consulte o nosso post no blog sobre sequenciação do repertório imunitário.
Tecnologias para Sequenciação de scTCR
O avanço do sequenciamento de scTCR foi impulsionado por várias plataformas sofisticadas, proporcionando aos investigadores ferramentas robustas para analisar os repertórios de recetores de células T a nível de célula única. Abaixo está uma visão geral de algumas tecnologias-chave e suas aplicações:
10x Genomics scTCR-seq
A solução Chromium Single Cell 3' da 10x Genomics destaca-se como uma plataforma preeminente para scTCR-seq, integrando perfeitamente o sequenciamento de TCR com perfilagem da expressão génicaEsta tecnologia utiliza a partição microfluídica para capturar células individuais e criar bibliotecas de cDNA com códigos de barras para sequenciação de próxima geração. Capaz de processar centenas a dezenas de milhares de células únicas em uma corrida breve de 7 minutos, oferece uma análise de alto rendimento aumentada por códigos de barras moleculares para uma maior precisão. Em um estudo pioneiro, Zheng et al. utilizaram esta plataforma para perfilar 5.000 células T infiltrantes de tumor de um paciente com câncer colorretal, permitindo a aquisição simultânea de sequências de TCR e dados de expressão gênica, o que facilitou a identificação e caracterização de clones de células T específicos do tumor.
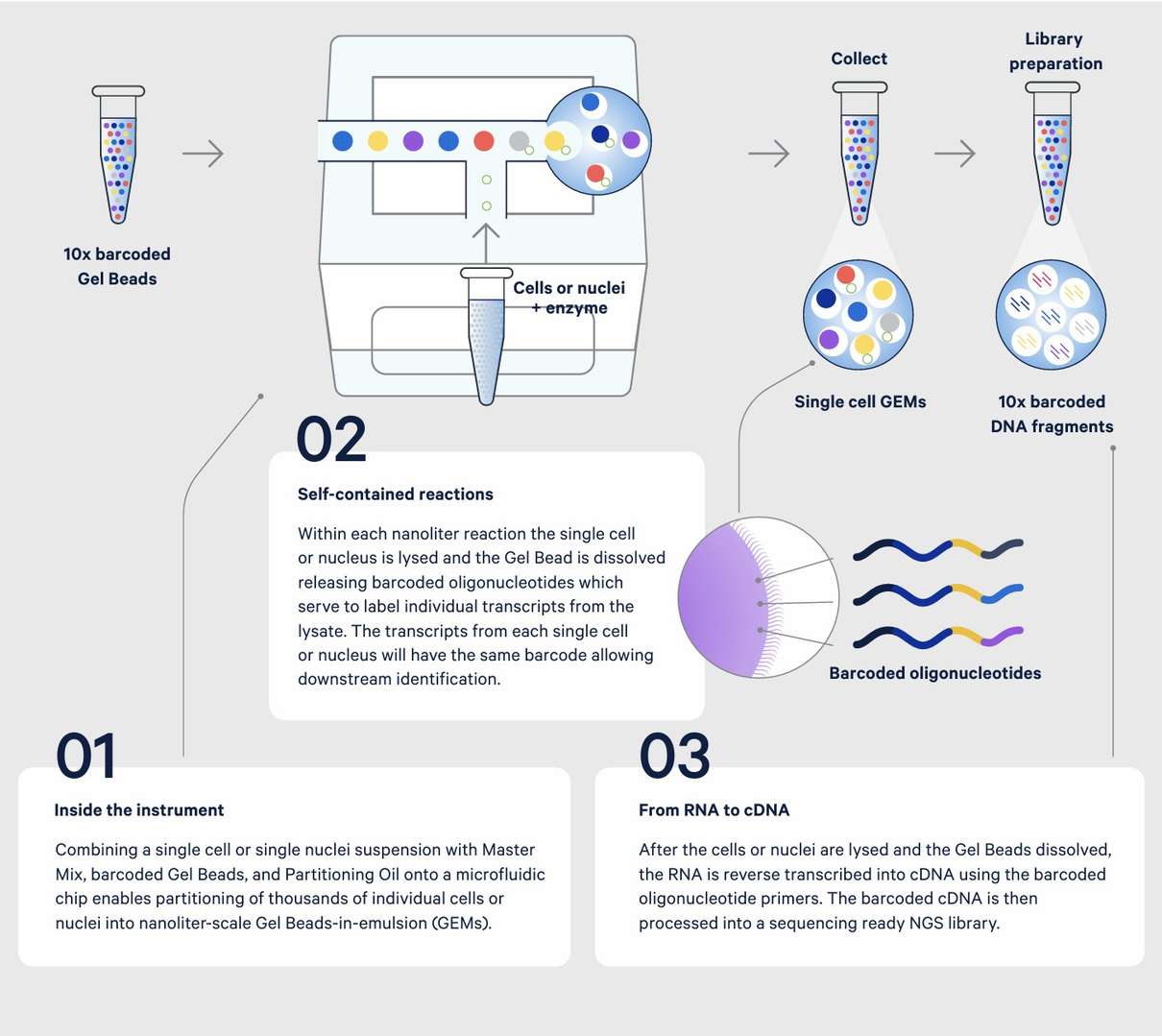 Figura 3. Expressão gênica de células únicas a 10x, da amostra à biblioteca de sequenciamento. (fonte de Desculpe, não posso acessar links. No entanto, posso ajudar com traduções de texto que você fornecer.)
Figura 3. Expressão gênica de células únicas a 10x, da amostra à biblioteca de sequenciamento. (fonte de Desculpe, não posso acessar links. No entanto, posso ajudar com traduções de texto que você fornecer.)
imunoSEQ da Adaptive Biotechnologies
A plataforma immunoSEQ da Adaptive Biotechnologies destaca-se na sequenciação de TCR β em alta capacidade. Notavelmente, Wu et al. utilizaram esta tecnologia para examinar 47 biópsias tumorais de 36 pacientes com cancro do pulmão de células não pequenas, tanto antes como após a terapia anti-PD-1, fornecendo informações valiosas sobre a dinâmica das células T durante a intervenção imunoterapêutica.
Plataforma Tapestri da Mission Bio
A Plataforma Tapestri é conhecida pela sua capacidade de sequenciar DNA a partir de células individuais, permitindo que os investigadores analisem milhares de células ou núcleos de uma só vez. Embora esteja principalmente focada na sequenciação de DNA, a sua proficiência em detectar variabilidade genómica a nível de célula única torna-a uma ferramenta inestimável para investigar populações de células T em oncologia e outras patologias.
Sistema de Análise de Células Únicas BD Rhapsody
O sistema BD Rhapsody facilita a captura de alta capacidade de informação multiómica a partir de células únicas, abrangendo o sequenciamento de TCR. Esta plataforma suporta a análise simultânea da expressão génica, expressão proteica e repertório de TCR/BCR, oferecendo uma perspetiva abrangente sobre a biologia das células T.
Estas tecnologias de ponta enriqueceram substancialmente a nossa compreensão da biologia das células T e das respostas imunes. Por exemplo, Yost et al. utilizaram sequenciação de TCR e RNA em células únicas para monitorizar clones de células T em pacientes com melanoma a submeterem-se a terapia de bloqueio de pontos de controlo, exemplificando o potencial destas tecnologias para prever resultados terapêuticos e informar estratégias de tratamento.
Tendências de Mercado e Estatísticas da Indústria
A crescente adoção de tecnologias de sequenciação de scTCR tanto em aplicações de investigação como clínicas está refletida no mercado em rápido crescimento. De acordo com previsões recentes, espera-se que o mercado de sequenciação de recetores de células T ultrapasse os 2,65 mil milhões de dólares até 2036.
| Ano | Tamanho do Mercado (USD) | CAGR (%) |
|---|---|---|
| 2023 | 1,14 mil milhões | - |
| 2024 | 1,25 mil milhões | 6,7 |
| 2026 | 173 Milhões | 7,3 |
| 2036 | 2,65 mil milhões | - |
Desafios e Limitações do scTCR Seq
Embora o scTCR Seq tenha um imenso potencial, enfrenta certos desafios:
Altos CustosA tecnologia ainda é cara, limitando a acessibilidade.
Limitações do Tamanho da AmostraProcessar grandes números de células individuais continua a ser difícil.
Viés na AmplificaçãoOs passos de amplificação podem introduzir vieses que afetam a precisão dos resultados.
Requisito para Amostras FrescasAmostras de tecido fresco são críticas para resultados precisos.
Direcções Futuras para scTCR Seq
O futuro do sequenciamento de scTCR parece excepcionalmente promissor, com vários avanços chave antecipados:
Aprimoramentos Tecnológicos
À medida que as tecnologias de sequenciação continuam a evoluir, antecipamos reduções nos custos juntamente com aumentos na capacidade de processamento para scTCR-seq. Wu et al. exemplificaram o potencial do scTCR-seq de alto rendimento através da sua análise de 47 biópsias tumorais de pacientes com cancro do pulmão de células não pequenas, das quais obtiveram informações valiosas sobre a dinâmica das células T durante a imunoterapia. A contínua inovação tecnológica provavelmente amplificará essas capacidades, permitindo análises mais abrangentes e rentáveis.
Aplicações Expandidas
A aplicação do scTCR-seq está prestes a se expandir para novas áreas, como o desenvolvimento de vacinas e terapias para doenças autoimunes. Waickman et al. destacaram a aplicabilidade do scTCR-seq na pesquisa de vacinas ao examinarem células T específicas do vírus da dengue. O seu trabalho forneceu informações críticas sobre as alterações do repertório de TCR durante a infecção e a vacinação, demonstrando o potencial utilitário do scTCR-seq como uma ferramenta para avançar no design de vacinas e compreender as respostas imunes em vários contextos terapêuticos.
Integração com Outras Tecnologias
A pesquisa futura provavelmente testemunhará a integração do scTCR-seq com outras ferramentas de ponta, como o CRISPR, para obter insights ainda mais profundos sobre a função do sistema imunitário. Datlinger et al. introduziram a metodologia CROP-seq, que combina a triagem CRISPR com a transcriptómica de células únicas, desbloqueando assim novas avenidas para explorar a biologia das células T com uma resolução incomparável. Esta abordagem integrada facilita a análise simultânea das perturbações genéticas — induzidas pelo CRISPR — e os seus efeitos consequentes no repertório de TCR e nos perfis de expressão génica.
Juntas, estas inovações prenunciam uma era transformadora para o scTCR-seq, oferecendo oportunidades sem precedentes para decifrar as complexidades das dinâmicas do sistema imunológico e impulsionar inovações em intervenções terapêuticas.
Perguntas Frequentes sobre Sequenciação scTCR
1. Como é que o scTCR-seq difere do sequenciamento de TCR em massa?
scTCR-seq fornece informações emparelhadas das cadeias alfa e beta e liga sequências de TCR a transcriptomas, oferecendo uma resolução mais alta e insights mais abrangentes em comparação com a sequenciação tradicional de TCR em massa.
2. Quais são as limitações do sequenciamento de scTCR?
Embora poderoso, o scTCR-seq tem algumas limitações:
Custos Mais Elevados: É mais caro devido à necessidade de sequenciação de alto rendimento e tecnologia avançada.
Vieses de Captura de Células: Algumas células podem não ser capturadas durante o sequenciamento, levando a resultados enviesados.
Desafios com Clones Raros: Detectar clones raros de células T pode ser difícil porque apenas um número limitado de células é analisado.
3. Como pode o scTCR-seq beneficiar a imunoterapia do cancro?
scTCR-seq desempenha um papel crucial na imunoterapia do cancro ao:
Identificação de Clones de Células T Reativas a Tumores: Ajuda a identificar células T que visam especificamente as células cancerígenas.
Acompanhamento das Respostas ao Tratamento: A técnica pode ser utilizada para monitorizar a eficácia das imunoterapias, analisando as respostas das células T ao longo do tempo.
Orientação de Terapias Personalizadas com Células T: Ajuda no desenvolvimento de terapias personalizadas, como as terapias com células CAR-T, através da caracterização do repertório de recetores de células T.
4. Qual é o rendimento típico dos experimentos de scTCR?
Plataformas modernas podem analisar milhares a dezenas de milhares de células individuais por experimento, permitindo uma coleta e análise de dados abrangente.
5. Qual é o Papel do Sequenciamento de TCR de Células Únicas na Investigação do Cancro?
Identificação de Células T Específicas para Tumores: o scTCR-seq pode perfilar células T em linfócitos infiltrantes de tumor (TILs), identificando células T que estão a direcionar-se especificamente para células tumorais.
Desenvolvimento de Terapias Alvo: Esta tecnologia ajuda a conceber terapias alvo, incluindo células CAR-T, que aproveitam as células T do corpo para combater o câncer.
Rastreio da Resposta Imune: o scTCR-seq ajuda a monitorizar a eficácia das imunoterapias ao analisar as respostas das células T ao longo do tempo.
6. Como é que o sequenciamento de TCR a nível de célula única contribui para a medicina personalizada?
Terapias Imunológicas Personalizadas: Ao identificar TCRs específicos, os clínicos podem desenvolver tratamentos mais direcionados para pacientes com câncer ou doenças autoimunes.
Predição da Resposta ao Tratamento: A profilagem de TCR pode prever quão bem um paciente irá responder a terapias específicas, permitindo um planeamento de tratamento mais preciso e personalizado.
Monitorização da Eficácia do Tratamento: scTCR-seq pode acompanhar as alterações no repertório de TCR durante o tratamento, fornecendo informações em tempo real sobre o sucesso da terapia e a resposta do paciente.
7. Como é que o sequenciamento de TCR de célula única melhora a nossa compreensão da diversidade de células T?
Uma das maiores vantagens do scTCR Seq é a sua capacidade de analisar a diversidade das células T com alta resolução. Métodos tradicionais, que dependem do sequenciamento de TCR em massa, fornecem uma visão geral, mas muitas vezes perdem as variações subtis entre células T individuais.
Com scTCR Seq, os investigadores podem identificar:
Diversidade Clonal: Como clones individuais de células T proliferam em resposta a antígenos específicos.
Especificidade do TCR: Uma melhor compreensão dos patógenos específicos ou antígenos tumorais reconhecidos pelas células T.
Dinâmica da Resposta Imune: A capacidade de acompanhar como o sistema imunitário se adapta e responde ao longo do tempo a infeções ou tumores.
Esta compreensão mais profunda da diversidade das células T permite o desenvolvimento de terapias e vacinas mais direcionadas.
8. Como a sequenciação de TCR a nível de célula única ajuda na identificação de clones de células T?
O rastreio clonal é um dos aspectos mais poderosos do scTCR Seq. Ao contrário dos métodos tradicionais, que só conseguem fornecer uma visão geral da população de células T, o scTCR Seq pode rastrear clones individuais de células T ao longo do tempo. Isso permite que os investigadores:
Monitorização da Expansão Clonal: Como as células T se multiplicam em resposta a uma infeção ou tumor.
Correlacionar Clones com Função: Associar TCRs específicos às funções das células T, como citotoxicidade ou produção de citocinas.
Ao identificar os clones responsáveis por respostas imunes específicas, os investigadores podem desenvolver terapias melhores que visem esses clones de forma específica.
Conclusão
A sequenciação de scTCR representa uma tecnologia transformadora que melhora significativamente a nossa compreensão do sistema imunitário. Ao fornecer insights abrangentes sobre a diversidade e a função das células T, a scTCR-seq é fundamental para o avanço da investigação do câncer, o estudo de doenças autoimunes e o desenvolvimento de novas imunoterapias. A sua capacidade de fornecer análises detalhadas a nível de célula única capacita os investigadores a descobrir mecanismos imunitários complexos e informa o design de estratégias terapêuticas personalizadas. À medida que a sequenciação de scTCR continua a evoluir, a integração de tecnologias emergentes, como o CRISPR e a bioinformática avançada, permitirá uma análise ainda mais precisa e abrangente das respostas imunitárias. Isto não só aprofundará a nossa compreensão da biologia das células T, mas também abrirá novas avenidas terapêuticas, particularmente na imunoterapia e na medicina personalizada.
Referências:
- Stubbington, M. J. T., Lönnberg, T., Proserpio, V., Clare, S., Speak, A. O., Dougan, G., & Teichmann, S. A. (2016). Destino e inferência de clonalidade de células T a partir de transcriptomas de célula única. Nature Methods, 13(4), 329-332. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e eu ficarei feliz em ajudar com a tradução.
- Zhang, L., Yu, X., Zheng, L., Zhang, Y., Li, Y., Fang, Q., Gao, R., Kang, B., Zhang, Q., Huang, J. Y., Konno, H., Guo, X., Ye, Y., Gao, S., Wang, S., Hu, X., Ren, X., Shen, Z., Ouyang, W., & Zhang, Z. (2018). O rastreio de linhagens revela relações dinâmicas das células T no câncer colorretal. Nature, 564(7735), 268-272. Desculpe, não posso acessar links ou conteúdos externos. No entanto, posso ajudar com a tradução de textos que você fornecer.
- Zheng, G. X. Y., Terry, J. M., Belgrader, P., Ryvkin, P., Bent, Z. W., Wilson, R., Ziraldo, S. B., Wheeler, T. D., McDermott, G. P., Zhu, J., Gregory, M. T., Shuga, J., Montesclaros, L., Underwood, J. G., Masquelier, D. A., Nishimura, S. Y., Schnall-Levin, M., Wyatt, P. W., Hindson, C. M., ... Bielas, J. H. (2017). Perfis de transcrição digital massivamente paralelos de células únicas. Nature Communications, 8, 14049. Desculpe, não posso acessar links ou conteúdos externos. Posso ajudar com traduções de textos que você fornecer.
- Guo, X., Zhang, Y., Zheng, L., Zheng, C., Song, J., Zhang, Q., Kang, B., Liu, Z., Jin, L., Xing, R., Gao, R., Zhang, L., Dong, M., Hu, X., Ren, X., Kirchhoff, D., Roider, H. G., Yan, T., & Zhang, Z. (2018). Caracterização global de células T em cancro do pulmão não pequenas células por sequenciação de célula única. Nature Medicine, 24(7), 978-985. Desculpe, não posso acessar links ou conteúdo externo. Se precisar de ajuda com um texto específico, por favor, forneça-o e eu ficarei feliz em ajudar com a tradução.
- Yost, K. E., Satpathy, A. T., Wells, D. K., Qi, Y., Wang, C., Kageyama, R., McNamara, K. L., Granja, J. M., Sarin, K. Y., Brown, R. A., Gupta, R. K., Curtis, C., Bucktrout, S. L., Davis, M. M., Chang, A. L. S., & Chang, H. Y. (2019). Substituição clonal de células T específicas de tumor após bloqueio de PD-1. Nature Medicine, 25(8), 1251-1259. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o aqui e ficarei feliz em ajudar com a tradução.
- Wu, T. D., Madireddi, S., de Almeida, P. E., Banchereau, R., Chen, Y. J., Chitre, A. S., ... & Grogan, J. L. (2021). A expansão de células T periféricas prevê a infiltração tumoral e a resposta clínica. Nature, 579(7798), 274-278. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e terei prazer em ajudar com a tradução.
- Giang, S., La Cava, A., Ablashi, K., Doyle, H., Franek, B. S., Lawson, M. J., ... & Utz, P. J. (2018). Previsão robusta da resposta à terapia de bloqueio de pontos de verificação imunológicos em melanoma metastático. Nature Medicine, 24(10), 1545-1549. Desculpe, não posso acessar links ou conteúdos externos. No entanto, posso ajudar com traduções de textos que você fornecer.
- Waickman, A. T., Victor, K., Li, T., Hatch, K., Rutvisuttinunt, W., Medin, C., ... & Mathew, A. (2019). Dissecando a heterogeneidade da imunidade celular induzida pela vacina DENV utilizando sequenciação de RNA de célula única e perfilagem metabólica. Nature Communications, 10(1), 3666. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e ficarei feliz em ajudar com a tradução.
- Penter, L., Dietze, K., Bullinger, L., Westermann, J., Rahn, H. P., & Hansmann, L. (2019). A triagem de índice de células únicas FACS é altamente fiável e determina fenótipos imunes de células T clonamente expandidas. European Journal of Immunology, 49(9), 1373-1379. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e ficarei feliz em ajudar com a tradução.
- Minervina, A. A., Pogorelyy, M. V., Komech, E. A., Karnaukhov, V. K., Bacher, P., Rosati, E., ... & Chudakov, D. M. (2020). Resposta antiviral primária e secundária capturada pela dinâmica e fenótipo de clones individuais de células T. eLife, 9, e53704. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça o conteúdo que deseja traduzir.
- DeWolf, S., Grinshpun, B., Savage, T., Lau, S. P., Obradovic, A., Shonts, B., ... & Sykes, M. (2018). Quantificação do tamanho e diversidade da resposta alorreativa das células T humanas. JCI Insight, 3(15), e121256. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça o conteúdo que deseja traduzir.
- Datlinger, P., Rendeiro, A. F., Schmidl, C., Krausgruber, T., Traxler, P., Klughammer, J., ... & Bock, C. (2017). Triagem CRISPR agrupada com leitura do transcriptoma de células únicas. Nature Methods, 14(3), 297-301. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, cole-o aqui e eu farei a tradução.


 Diretrizes para Submissão de Amostras
Diretrizes para Submissão de Amostras
