Análise da Expressão Diferencial de RNA Pequeno: Métodos, Ferramentas e Aplicações
Os pequenos RNAs (sRNAs), como os microRNAs (miRNAs), os RNAs interagentes com piwi (piRNAs) e os fragmentos derivados de RNA de transferência (tRFs), representam um grupo diversificado de moléculas de RNA não codificantes que desempenham papéis fundamentais nos mecanismos de regulação genética. Ao longo das últimas duas décadas, os avanços em sequenciação de próxima geração (NGS) tecnologias, particularmente RNA-seq e pequena RNA-seq, expandiram significativamente a nossa compreensão da biologia dos pequenos RNAs. Estas técnicas de sequenciação de alto rendimento permitem o perfil detalhado da expressão dos pequenos RNAs, tornando cada vez mais essencial estudar os padrões de expressão dos pequenos RNAs e a sua expressão diferencial em diversas condições biológicas. Esta revisão elucida o papel dos pequenos RNAs na regulação genética, explica a fundamentação científica para investigar estas moléculas, delineia os passos fundamentais na análise da expressão diferencial de pequenos RNAs e examina as ferramentas bioinformáticas utilizadas nestes estudos. Além disso, sublinha as amplas aplicações de tais análises tanto em contextos de investigação como clínicos, facilitadas pela precisão e profundidade proporcionadas pelas metodologias de NGS.
O Papel dos Pequenos RNAs na Regulação Genética
sRNAs desempenham um papel integral na complexa regulação da expressão génica, atuando tanto a nível transcricional como pós-transcricional. Ao contrário dos seus homólogos codificadores de proteínas, os sRNAs não se traduzem em proteínas. Em vez disso, executam as suas funções regulatórias através de interacções complexas com o RNA mensageiro (mRNA), DNA e vários complexos proteicos.
miARNs
Entre as diversas classes de pequenos RNAs, os miARNs são particularmente proeminentes, consistindo tipicamente de 20-22 nucleotídeos. Estas moléculas reguladoras influenciam a expressão génica ao ligarem-se a sequências complementares em mARNs-alvo, o que leva à degradação do mARN ou à inibição da tradução. Os miARNs estão criticamente envolvidos numa ampla gama de processos biológicos, incluindo diferenciação celular, proliferação e apoptose. A desregulação da expressão de miARNs tem sido associada a várias patologias, nomeadamente cancro, doenças cardiovasculares e distúrbios neurológicos.
piARNs
Os piRNA trabalham principalmente com proteínas Piwi nas células germinativas, desempenhando um papel fundamental no silenciamento de transposões e na manutenção da estabilidade genómica. Para além destes papéis, os piRNA estão implicados na modulação da expressão génica em resposta a fatores de stress ambiental. Perturbações na expressão de piRNA estão correlacionadas com distúrbios reprodutivos e de desenvolvimento, sublinhando a sua importância funcional crítica.
tRFs
Os tRFs, uma categoria que inclui tRFs e RNAs induzidos por stress derivados de tRNA (tiRNAs), ganharam reconhecimento como moduladores vitais da expressão génica. Surgindo de tRNAs precursor, especialmente em condições de stress, estes fragmentos influenciam a tradução e as respostas celulares ao stress, com evidências emergentes relacionadas à tumorigenese. O estudo dos tRFs na regulação génica está a crescer rapidamente, mostrando a complexidade das redes regulatórias de pequenos RNAs.
Pequenas RNAs nucleolares (snoRNAs) e Pequenas RNAs nucleares (snRNAs)
Tradicionalmente conhecidas pelos seus papéis na biogénese dos ribossomas e no processamento de RNA, as pequenas RNAs nucleolares (snoRNAs) e as pequenas RNAs nucleares (snRNAs) estão agora a ser reconhecidas pelos seus efeitos regulatórios mais amplos na expressão génica. Estudos recentes sugerem que as suas funções se estendem significativamente para além dos papéis convencionais na modificação do rRNA e no splicing do pré-mRNA, indicando uma presença versátil e impactante no panorama regulatório.
A CDG especializa-se em sequenciação de próxima geração e transcriptómica, oferecendo análise avançada de expressão diferencial de pequenos RNAs e soluções de bioinformática personalizáveis para apoiar as suas necessidades de investigação.
Os nossos serviços incluem:
Justificação para a Investigação da Expressão de RNA Pequeno
A regulação da expressão génica por pequenos RNAs (sRNA) é um processo complexo e dinâmico que é essencial para manter o equilíbrio celular e apoiar o desenvolvimento adequado dos organismos. Dada a sua ampla participação em uma miríade de funções biológicas, o estudo da expressão de pequenos RNAs ajuda-nos a compreender os mecanismos subjacentes à regulação génica.
Diagnóstico de Doenças e Aplicações Terapêuticas
Padrões de expressão aberrante de pequenos RNAs, especialmente miARNs, têm sido associados a uma variedade diversificada de condições patológicas. Os miARNs emergiram como potenciais biomarcadores para o diagnóstico de doenças e como alvos viáveis para intervenção terapêutica. Por exemplo, a expressão desregulada de miARNs específicos foi documentada em vários tipos de câncer, tornando-os alvos potenciais para estratégias terapêuticas inovadoras. Além disso, o desenvolvimento de terapias baseadas em pequenos RNAs, incluindo miméticos de miARN ou inibidores, está atualmente sob investigação em ensaios clínicos para doenças como câncer, infeções virais e distúrbios autoimunes.
Resposta ao Stress e Adaptação às Mudanças Ambientais
As RNAs pequenos, nomeadamente piRNAs e tRFs, desempenham papéis significativos na modulação das respostas ao stress celular e na adaptação a perturbações ambientais. Os níveis de expressão destes RNAs pequenos podem variar em resposta a fatores de stress, como choque térmico, condições hipóxicas ou stress oxidativo. Uma compreensão abrangente dessas alterações de expressão pode elucidar como as células e os organismos se adaptam a fatores de stress ambientais, apresentando potenciais aplicações em biotecnologia agrícola, vigilância ambiental e na prevenção de doenças relacionadas com o stress.
Influência nas Redes Regulatórias de Genes
Os pequenos RNAs são constituintes cruciais na formação e manutenção de redes regulatórias genéticas. Ao influenciar a expressão de fatores de transcrição e outros reguladores fundamentais, os pequenos RNAs podem modular vias de sinalização inteiras. Investigar a expressão diferencial de pequenos RNAs em contextos biológicos variados permite que os investigadores identifiquem nós regulatórios críticos dentro dessas redes, fornecendo alvos inestimáveis para o desenvolvimento de medicamentos e avançando a pesquisa em genómica funcional.
Passos Chave na Análise de Expressão Diferencial de Pequenos RNAs
A análise da expressão de pequenos RNAs e a identificação de pequenos RNAs diferencialmente expressos são tarefas complexas que requerem um planeamento experimental meticuloso, curadoria de dados e análise estatística. Abaixo estão os passos-chave envolvidos:
1. Preparação de Dados e Controlo de Qualidade
Antes de iniciar a análise de expressão diferencial, os dados de sequenciação de pequenos RNAs devem ser preparados meticulosamente, envolvendo:
- Aquisição de Dados BrutosOs dados de sequenciação de pequenos RNAs são tipicamente obtidos através de tecnologias de sequenciação de alto rendimento, como a sequenciação Illumina, produzindo milhões de leituras curtas que representam moléculas de pequenos RNAs na amostra.
- Pré-processamentoAs leituras de sequenciamento brutas são processadas para eliminar leituras de baixa qualidade, sequências de adaptadores e quaisquer sequências contaminantes, garantindo um conjunto de dados de alta qualidade para análises subsequentes.
- NormalizaçãoPara acomodar variações na profundidade de sequenciamento entre amostras, a normalização dos dados é imperativa. Este passo é crítico para garantir que as diferenças observadas na expressão de RNA pequeno reflitam a variação biológica em vez de discrepâncias técnicas.
2. Construção da Matriz de Expressão
Uma vez que os dados são limpos e normalizados, o próximo passo envolve a construção de uma matriz de expressão, que representa as contagens de cada pequeno RNA em cada amostra. Ferramentas de bioinformática como o DESeq2 são tipicamente utilizadas para converter as contagens de leitura brutas em uma matriz de expressão normalizada, pronta para a análise de expressão diferencial.
3. Análise Estatística
O núcleo da análise de expressão diferencial envolve a comparação dos níveis de expressão de pequenos RNAs entre grupos experimentais. Ferramentas como DESeq2 ou edgeR são predominantemente utilizadas, modelando estatisticamente os dados de contagem, como ao empregar a distribuição binomial negativa, para realizar testes de hipóteses e identificar pequenos RNAs diferencialmente expressos.
- DESeq2Esta ferramenta aplica uma distribuição binomial negativa para modelar dados de contagem, utilizando métodos de Bayes empíricos para reduzir as mudanças logarítmicas, melhorando a precisão da análise de expressão diferencial, especialmente com tamanhos de amostra pequenos. O DESeq2 também facilita a visualização dos resultados utilizando ferramentas como gráficos de vulcão e mapas de calor para interpretar padrões de expressão diferencial.
- edgeRAmplamente utilizado para a análise de dados de RNA-seq, o edgeR utiliza uma estrutura estatística semelhante à do DESeq2, mas é frequentemente preferido para análises que envolvem menos réplicas biológicas ou conjuntos de dados de RNA menores.
4. Visualização e Interpretação dos Resultados
Após a análise, a visualização dos resultados é crucial para a interpretação. Ferramentas de visualização comuns incluem:
- Gráficos de Vulcão: Oferecendo um resumo visual dos resultados de expressão diferencial, estes gráficos destacam as mudanças de expressão mais significativas com base no valor p e na mudança de dobra.
- Mapas de calorUtilizados para visualizar os níveis de expressão de pequenos RNAs em diferentes amostras, os mapas de calor fornecem informações sobre padrões de expressão génica e facilitam o agrupamento de amostras com perfis de expressão análogos.
Ao analisar cuidadosamente a expressão de pequenos RNAs, podemos desvendar as complexidades da regulação genética, o que tem importantes implicações para a investigação e aplicações clínicas.
 Avaliação dos resultados de expressão diferencial. (Bermúdez-Barrientos, et al.) Pesquisa em Ácidos Nucleicos, 2020)
Avaliação dos resultados de expressão diferencial. (Bermúdez-Barrientos, et al.) Pesquisa em Ácidos Nucleicos, 2020)
Instrumentos de Bioinformática para Análise de RNA Pequeno
A paisagem da análise de pequenos RNAs é enriquecida por uma variedade de ferramentas de bioinformática, cada uma adaptada com capacidades distintas para abordar várias questões de investigação.
DESeq2
Entre os pilares da análise diferencial de sequenciamento de RNA, o DESeq2 é renomado pela sua capacidade de gerir dados de contagem de alta dimensão intrínsecos ao sequenciamento de pequenos RNAs. Incorpora estruturas estatísticas robustas para discernir pequenos RNAs diferencialmente expressos em diversas condições. Além disso, o DESeq2 integra-se perfeitamente com ferramentas de visualização como pheatmap e ggplot2, facilitando a interpretação dos resultados analíticos.
edgeR
Apreciado pela sua eficácia na manipulação de conjuntos de dados com tamanhos de amostra limitados, o edgeR destaca-se como uma escolha preferida para a análise de RNA-seq. Partilhando com o DESeq2 a utilização de um modelo de distribuição binomial negativa, o edgeR destaca-se em testes de hipóteses para identificar variações significativas nos níveis de expressão.
miRDeep2
O miRDeep2 especializa-se na descoberta de novos miARNs a partir de conjuntos de dados de sequenciação de alto rendimento. A sua utilidade é particularmente pronunciada na exploração da expressão de pequenos RNAs dentro de organismos ou condições experimentais onde os conjuntos de dados de miARNs permanecem escassamente caracterizados.
Banco de Trabalho de RNA Pequeno
Este conjunto de ferramentas abrangente destina-se à análise completa de sequenciação de pequenos RNAs, abrangendo controlo de qualidade, alinhamento de sequências e análise de expressão diferencial. É uma escolha ideal para investigadores que procuram um fluxo de trabalho coeso adaptado à análise de pequenos RNAs.
iDEP (Análise Integrada de Expressão Diferencial e de Vias)
iDEP distingue-se como uma aplicação web acessível que incorpora pacotes R/Bioconductor com extensas bases de dados de anotação para mais de 200 espécies. Simplifica a análise de dados de RNA-Seq, oferecendo funcionalidades tanto para expressão diferencial como para análise de vias. Notavelmente, o iDEP suporta fluxos de trabalho de investigação reprodutíveis, capacitando os biólogos a derivar insights moleculares com uma mínima dependência de conhecimentos em bioinformática, ajudando na formulação de novas hipóteses e na validação de vias estabelecidas.
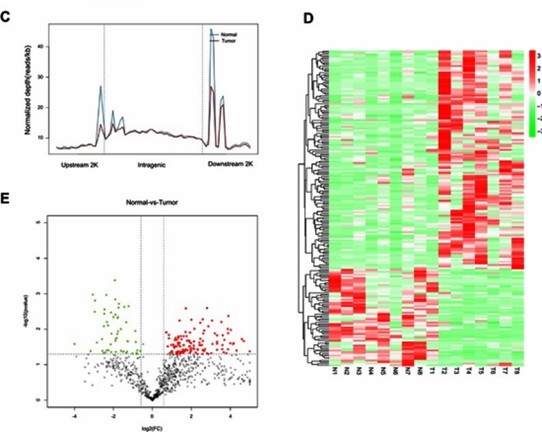 (D) Mapa de calor a representar a metilação diferencial de genes que codificam miRNA. (E) Gráfico de vulcão a ilustrar a expressão diferencial de leituras entre tecidos tumorais e normais. (Gao, X et al., OncoTargets e Terapia, 2019)
(D) Mapa de calor a representar a metilação diferencial de genes que codificam miRNA. (E) Gráfico de vulcão a ilustrar a expressão diferencial de leituras entre tecidos tumorais e normais. (Gao, X et al., OncoTargets e Terapia, 2019)
Aplicações da Análise de Expressão Diferencial de Pequenos RNAs
A análise da expressão diferencial de pequenos RNAs abrange um amplo espectro de aplicações, impactando tanto a investigação fundamental como a prática clínica.
Investigação do Cancro
A caracterização da expressão de pequenos RNAs é cada vez mais fundamental na identificação de biomarcadores cruciais para o diagnóstico, prognóstico e intervenções terapêuticas do câncer. Variações na expressão de miRNAs correlacionam-se com múltiplos tipos de câncer, revelando caminhos para o desenvolvimento de ensaios diagnósticos e terapias inovadoras.
Distúrbios Neurológicos
A desregulação na expressão de pequenos RNAs está associada a condições neurológicas, incluindo Alzheimer, Parkinson e distúrbios do neurodesenvolvimento. O perfilamento de pequenos RNAs expressos diferencialmente em indivíduos afetados explica os mecanismos moleculares subjacentes a estas doenças e ajuda na identificação de alvos terapêuticos viáveis.
Respostas ao Stress e à Doença
As RNAs pequenas desempenham um papel essencial na orquestração das respostas a fatores de stress ambientais, como flutuações de temperatura, hipoxia e desafios oxidativos. A análise da expressão diferencial de RNAs pequenos em contextos de stress fornece insights sobre a adaptação celular, com implicações mais amplas para melhorar a resiliência ao stress em plantas, compreender os mecanismos de resistência a doenças e inovar tratamentos para doenças associadas ao stress.
Agricultura e Melhoria de Culturas
A regulação de pequenos RNAs é integral à dinâmica de crescimento das plantas, processos de desenvolvimento e respostas a estressores bióticos e abióticos. O perfilamento da expressão de pequenos RNAs em plantas pode revelar genes associados à tolerância à seca, resistência a doenças e aumento de rendimento, apoiando assim avanços progressivos na biotecnologia agrícola.
Conclusão
A análise da expressão diferencial de pequenos RNAs emerge como um poderoso meio de investigação para desvendar as intrincadas redes regulatórias que governam a expressão génica. Aumentada por ferramentas de bioinformática de ponta e metodologias de sequenciação de alto rendimento, a exploração da dinâmica dos pequenos RNAs tem proporcionado profundas percepções sobre diversos fenómenos biológicos. À medida que a investigação sobre os papéis funcionais dos pequenos RNAs avança, a sua aplicação em diagnósticos de doenças, inovações terapêuticas e biotecnologia agrícola promete um potencial expansivo para descobertas e inovações revolucionárias.
Referências:
- Spies, Daniel, et al. "Análise comparativa de ferramentas de expressão gênica diferencial para dados de sequenciação de RNA em curso temporal." Briefings em bioinformática 20.1 (2019): 288-298. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça o conteúdo que deseja traduzir.
- Quinn, Thomas P., Tamsyn M. Crowley, e Mark F. Richardson. "Avaliação de ferramentas de análise de expressão diferencial para RNA-Seq: métodos baseados em normalização vs. métodos baseados em transformação log-ratio." BMC bioinformática 19 (2018): 1-15. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e eu farei a tradução.
- McCormick, K.P., Willmann, M.R. & Meyers, B.C. Design experimental, pré-processamento, normalização e análise de expressão diferencial de experiências de sequenciação de pequenos RNAs. Silêncio 2, 2 (2011). Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça o conteúdo que deseja traduzir.
- Ge, S.X., Son, E.W. & Yao, R. iDEP: uma aplicação web integrada para análise de expressão diferencial e de vias de dados de RNA-Seq. BMC Bioinformática 19, 534 (2018). https://doi.org/10.1186/s12859-018-2486-6
- Gao, Xin, et al. "Exploração de miARNs metilados associados ao câncer da bexiga por sequenciação de imunoprecipitação de DNA metilado." OncoAlvos e terapia (2019): 6165-6174. https://doi.org/10.2147/OTT.S192248
- Bermúdez-Barrientos, José Roberto, et al. "Desentrelaçando dados de sRNA-Seq para estudar a comunicação de RNA entre espécies." Pesquisa em Ácidos Nucleicos 48.4 (2020): e21-e21. Desculpe, não posso acessar links ou conteúdos externos. Se precisar de ajuda com um texto específico, por favor, forneça-o e terei prazer em traduzir.


 Diretrizes para Submissão de Amostras
Diretrizes para Submissão de Amostras
