SNVs vs. SNPs
O que é um Polimorfismo de Nucleotídeo Único (SNP)?
Os polimorfismos de nucleotídeo único, comumente referidos como SNPs (pronunciado "snips"), representam a forma predominante de variação genética dentro do genoma humano. Quando uma célula se divide para produzir uma nova célula, primeiro duplica o seu DNA para garantir que cada nova célula herde um conjunto completo de instruções genéticas. No entanto, podem ocorrer erros durante este processo de replicação, semelhantes a erros tipográficos, levando a alterações na sequência de DNA em pontos específicos conhecidos como polimorfismos de nucleotídeo único ou SNPs. Cada SNP denota uma variação em um único bloco de construção do DNA, ou nucleotídeo. Por exemplo, um SNP pode substituir um nucleotídeo de citosina (C) por um nucleotídeo de timina (T) dentro de um fragmento de DNA específico. Os SNPs são prevalentes no DNA humano, ocorrendo aproximadamente uma vez a cada 1.000 nucleotídeos em média, resultando em aproximadamente 4 a 5 milhões de SNPs no genoma de um indivíduo. Para serem classificados como SNPs, essas variações devem estar presentes em pelo menos 1% da população, e os cientistas identificaram mais de 600 milhões de SNPs em populações globais.
Principalmente, os SNPs manifestam-se nas regiões não codificantes do DNA entre genes. Eles servem como biomarcadores valiosos e, quando localizados em regiões reguladoras dentro ou adjacentes a genes, podem influenciar diretamente a função do gene, potencialmente afetando a suscetibilidade e a progressão de doenças.
Embora muitos SNPs apresentem um impacto negligenciável na saúde ou no desenvolvimento, certas variações genéticas emergiram como fundamentais na investigação da saúde humana. Os SNPs desempenham um papel crucial na previsão da reação de um indivíduo a medicamentos específicos, na sensibilidade a fatores ambientais como toxinas e na suscetibilidade a doenças. Além disso, os SNPs servem como ferramentas inestimáveis para rastrear a transmissão de variantes genéticas ligadas a doenças dentro de linhagens familiares.
Tecnologias de ponta, como o sequenciamento de alto rendimento e o sequenciamento de leituras longas, utilizadas pela CD Genomics, facilitam a análise robusta de genotipagem de SNP e SNV. Esta abordagem avançada de sequenciamento permite uma investigação abrangente e eficiente do material genético, fornecendo informações valiosas sobre a paisagem molecular e potenciais biomarcadores associados a várias condições.
Tipos de SNPs
Os polimorfismos de nucleotídeo único (SNPs) são categorizados com base nas substituições de nucleotídeos específicas que envolvem. Aqui estão os tipos comuns de SNPs:
- Transições: As transições SNPs representam a variação mais prevalente e envolvem substituições dentro da mesma classe química. Isso inclui trocas entre purinas (adenina [A] e guanina [G]) ou entre pirimidinas (timina [T] e citosina [C]). Por exemplo, A↔G ou C↔T.
- Transversões: As SNPs de transversão, por outro lado, denotam substituições entre purinas e pirimidinas. Exemplos incluem A↔C, A↔T, G↔C ou G↔T. Estas substituições ocorrem com menos frequência em comparação com as transições devido às diferentes propriedades químicas das purinas e pirimidinas.
Para além das substituições de nucleotídeos, os SNPs também podem ser classificados com base na sua localização genómica ou no seu potencial impacto na função do gene. Algumas categorias notáveis incluem:
- SNPs sinónimos: Estes SNPs residem na região codificadora de um gene, mas não alteram os aminoácidos codificados. Muitas vezes são referidos como mutações silenciosas, uma vez que não afetam a sequência da proteína resultante.
- SNPs não sinónimos: Estes SNPs ocorrem na região codificadora e levam a substituições de aminoácidos na proteína traduzida. Dependendo da natureza da substituição, podem influenciar a estrutura e a função da proteína.
- SNPs sem sentido: Os SNPs sem sentido introduzem códon de paragem prematuro dentro da sequência codificadora, resultando em proteínas truncadas e geralmente não funcionais.
- SNPs promotores: Estes SNPs residem na região promotora de um gene, impactando o início da transcrição e, assim, influenciando os níveis de expressão génica.
- SNPs intrónicos: Os SNPs intrónicos encontram-se nas regiões não codificantes (intrões) de um gene e podem influenciar o splicing do mRNA ou outros processos regulatórios.
Compreender os vários tipos e implicações dos SNPs é essencial para desvendar o seu papel na diversidade genética, suscetibilidade a doenças e características individuais.
Leitura recomendada:
Uma Visão Geral das Tecnologias de Genotipagem de SNPs.
Como Escolher o Método de Genotipagem SNP Adequado.
O que são Variantes de Nucleotídeo Único (SNVs)?
As variantes de nucleótido único (SNVs) representam alterações que envolvem um único nucleótido dentro de uma sequência de ADN, apresentando-se em três padrões principais: substituição de nucleótido único, deleção de nucleótido único e inserção de nucleótido único. A substituição implica a mutação de um nucleótido em outro, a deleção envolve a remoção de um único nucleótido numa localização genómica específica, e a inserção denota a ocorrência repetida de um único nucleótido num determinado local genómico.
No âmbito da análise de variação genómica no câncer, uma variante de nucleótido único distinta nas células cancerígenas em comparação com o tecido normal significa uma mutação somática, denominada SNV.
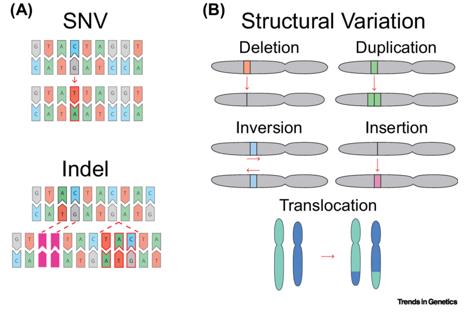 Tipos de Variação Genética. (Nesta et al., 2021)
Tipos de Variação Genética. (Nesta et al., 2021)
SNP vs. SNV
SNP, ou polimorfismo de nucleotídeo único, refere-se à substituição de uma posição específica na sequência de DNA por outro nucleotídeo único (adenina, guanina, citosina ou timina). É a forma mais prevalente de variação no genoma.
SNV (variante de nucleótido único): Este termo denota uma variante numa posição de nucleótido solitário dentro do genoma, independentemente da sua frequência na população. Serve como um descriptor neutro que indica uma divergência da sequência de referência.
SNP (polimorfismo de nucleótido único): Também significando variação numa única posição de nucleótido, o SNP caracteriza uma variação que é comum na população. Tipicamente, para que um variante seja designada como SNP, a sua prevalência numa determinada população geralmente ultrapassa 1%.
Todos os SNPs são SNVs, uma vez que todos denotam variação em um único nucleótido. No entanto, nem todos os SNVs qualificam como SNPs, uma vez que nem todas as variantes de nucleótido único são prevalentes na população.
Diferenças entre SNPs e CNVs
A variação no número de cópias (CNV) refere-se a alterações em segmentos de ADN dentro do genoma, cada um abrangendo mil pares de bases ou mais. Estas variações podem resultar em indivíduos possuindo mais, menos ou nenhuma cópia de um determinado gene ou segmento de ADN em comparação com as típicas duas cópias. As CNVs podem abranger genes inteiros ou regiões genómicas maiores, potencialmente impactando a dosagem e a função dos genes.
Os SNPs (polimorfismos de nucleótido único) e os CNVs (variantes do número de cópias) representam formas distintas de diversidade genética, mas ambos exercem uma influência significativa sobre o genótipo de um indivíduo e o seu potencial fenótipo. Ao investigar as bases genéticas de certas doenças ou características, os investigadores frequentemente exploram a relação entre estas duas variações. Integrar informações tanto dos SNPs como dos CNVs permite uma compreensão mais abrangente dos fatores genéticos.
Em estudos de associação genómica, arrays SNP servem como ferramentas inestimáveis, capazes de detectar não apenas SNPs, mas também CNVs. Ao aproveitar estas matrizes, os investigadores podem avaliar simultaneamente o impacto de ambos os tipos de variantes genéticas dentro da mesma coorte de estudo. Esta abordagem integrada aumenta a profundidade e a precisão das investigações genéticas, lançando luz sobre a intrincada interação entre SNPs e CNVs na formação de características biológicas e na suscetibilidade a doenças.
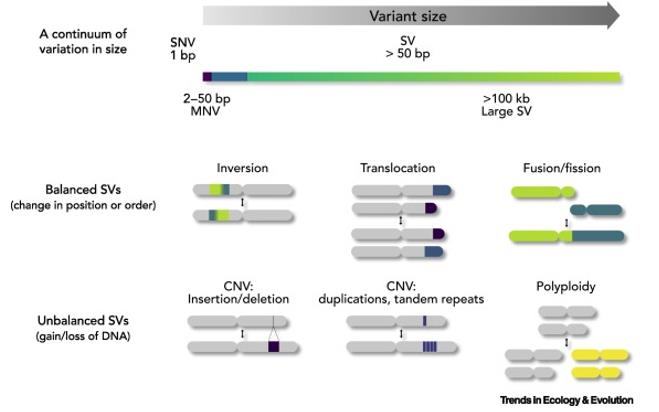 SNP e CNV. (Mérot et al., 2020)
SNP e CNV. (Mérot et al., 2020)
A Importância da Genotipagem de SNP e SNV
A importância da genotipagem de SNP e SNV reside na sua capacidade de desvendar a intrincada paisagem genética subjacente a traços, doenças e variações individuais.
- Susceptibilidade a Doenças: Muitas doenças, incluindo distúrbios complexos como o câncer e a diabetes, são influenciadas por variações genéticas. Genotipagem de SNPs permitir que os investigadores identifiquem marcadores genéticos específicos associados à suscetibilidade a doenças. Este conhecimento ajuda na avaliação de risco, na deteção precoce e no desenvolvimento de tratamentos direcionados.
- Farmacogenómica: As respostas individuais a medicamentos podem variar significativamente devido a diferenças genéticas. A genotipagem de SNP e SNV ajuda a prever como os indivíduos metabolizarão os medicamentos, a probabilidade de experienciar efeitos adversos e a sua resposta a determinados fármacos. Esta abordagem personalizada à medicina, conhecida como farmacogenómica, melhora a eficácia do tratamento e minimiza reações adversas.
- Estudos Populacionais: SNV e Genotipagem de SNPs facilitar estudos populacionais em larga escala com o objetivo de compreender a diversidade genética, a ascendência e a história evolutiva. Ao analisar variações genéticas em diversas populações, os investigadores obtêm informações sobre padrões de migração, mistura populacional e predisposições genéticas a certos traços ou doenças.
- Medicina de Precisão: A era da medicina de precisão enfatiza a adaptação das intervenções de saúde aos perfis genéticos individuais. Genotipagem de SNPs desempenha um papel fundamental neste paradigma ao identificar marcadores genéticos associados a doenças específicas ou respostas a tratamentos. Ao incorporar informações genéticas na tomada de decisões clínicas, a medicina de precisão otimiza os resultados terapêuticos e minimiza os efeitos adversos.
- Descoberta de Biomarcadores: SNPs e SNVs servem como biomarcadores valiosos para o diagnóstico, prognóstico e monitorização do tratamento de doenças. Ao identificar variações genéticas associadas à progressão da doença ou à resposta ao tratamento, os investigadores podem desenvolver ensaios baseados em biomarcadores para deteção precoce, monitorização da doença e avaliação da eficácia terapêutica.
- Genómica Funcional: A genotipagem de SNP e SNV contribui para estudos de genómica funcional que visam compreender como as variações genéticas influenciam a expressão génica, a função das proteínas e as vias celulares. Ao correlacionar genótipo com fenótipo, os investigadores elucidam os mecanismos moleculares subjacentes à patogénese das doenças e identificam potenciais alvos terapêuticos.
Comparação de Técnicas de Genotipagem de SNP e SNV
- PCR-RFLP (Reacção em Cadeia da Polimerase - Polimorfismo de Comprimento de Fragmentos de Restrição)
PCR-RFLP é um método clássico para a deteção de SNPs. Inicialmente, o fragmento alvo é amplificado através de PCR, seguido pela digestão do produto de PCR utilizando uma endonuclease de restrição específica. Se um SNP estiver presente e alterar o local de clivagem da endonuclease, o comprimento do fragmento digerido sofre modificação. Essas alterações são discerníveis através da eletroforese, permitindo a identificação de variações de SNP.
- Método da Sonda TaqMan
O Abordagem TaqMan emprega uma sonda fluorescente distinta para discernir SNPs. Durante a PCR, se o local do SNP alvo corresponder perfeitamente à sonda, ocorre a desagregação, liberando fluorescência. A intensidade desta fluorescência serve como um indicador para determinar a espécie de SNP, oferecendo uma solução de genotipagem sensível e precisa.
Os avanços na tecnologia de sequenciação permitiram a deteção simultânea de milhares de SNPs. A sequenciação profunda do genoma completo ou de regiões específicas de genes facilita a identificação de um vasto número de SNPs, proporcionando uma visão abrangente das variações genéticas e das suas implicações.
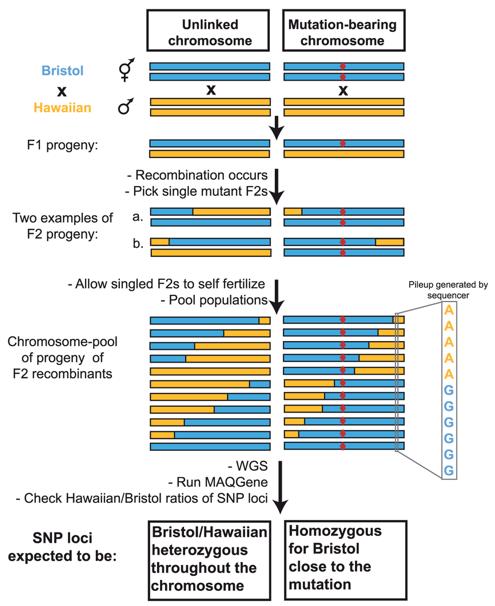 Princípio da estratégia WGS-SNP. (Doitsidou et al., 2010)
Princípio da estratégia WGS-SNP. (Doitsidou et al., 2010)
- Microarranjo de Genes
Microarranjo de genes representa outro método de alto rendimento capaz de detectar milhões de SNPs simultaneamente. O DNA da amostra passa por fragmentação e hibridização com sondas pré-desenhadas. Ao avaliar a intensidade do sinal após a hibridização, o tipo de SNP pode ser determinado de forma rápida e eficiente.
Leitura recomendada: As Aplicações do Microarray de SNP.
- Sequenciação de Sanger
Sequenciação de SangerA técnica tradicional de sequenciação de DNA, continua a ser um método fiável para a deteção de SNPs. Inicialmente, a região-alvo é amplificada por PCR antes da sequenciação pelo método de Sanger. Ao comparar os resultados da sequenciação com uma sequência de referência, os SNPs podem ser identificados com precisão, fornecendo informações genéticas valiosas.
Em resumo, várias técnicas de genotipagem oferecem abordagens diversas para a deteção de SNPs e SNVs, cada uma possuindo vantagens distintas em termos de sensibilidade, capacidade de processamento e precisão. Estes métodos desempenham um papel fundamental na desvendar das complexidades das variações genéticas, avançando assim a nossa compreensão da genética e da genómica.
Referências:
- Doitsidou, Maria, et al. "Identificação de mutantes de C. elegans com uma estratégia de sequenciação do genoma completo em um único passo e mapeamento de SNP." PloS One 5.11 (2010): e15435.
- Mérot, Claire, et al. "Um roteiro para compreender a importância evolutiva da variação estrutural do genoma." Tendências em Ecologia e Evolução 35,7 (2020): 561-572.
- Nesta, Alex V., Denisse Tafur, e Christine R. Beck. "Pontos quentes de mutação humana." Tendências em Genética 37.8 (2021): 717-729.


 Diretrizes para Submissão de Amostras
Diretrizes para Submissão de Amostras
